Análise exploratória (EDA) e Manipulação de dados: Dino dataset
Análise exploratória (EDA) e Manipulação de dados com o intuito de gerar insights a respeito de um pequeno dataset sobre dinossauros (maioria de variáveis categóricas).
O dataset foi obtido a partir de um processo de webscraping do site do Museu de História Nacional , realizado por outro usuário, ao qual eu descobri aleatoriamente. Assim, curioso e obcecado por dinossauros, resolvi unir o útil ao agradável e aprimorar meu conhecimento em EDA com um assunto que me agrada. Como é um dataset pequeno e majoritariamente constituído de variáveis qualitativas, trabalhei apenas na geração de insights, sem aplicar nenhum modelo preditivo.
O pequeno projeto aprimorou minhas skills na manipulação de dados e ampliou minha capacidade de gerar análises visualmente interessantes. O interessante da análise com Python é que, diferente de outras ferramentas, como Excel/Bi/Tableau, você tem uma maior versatilidade na hora de manipular/separar/excluir dados, além do potencial de análises preditivas, o que faz com que o conhecimento da linguagem torne-se muito positivo para quem gosta de trabalhar analisando dados.
É de praxe começar importando bibliotecas de frequente uso.
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
import seaborn as sns
import datetime as dt
import warnings
warnings.filterwarnings('ignore')
df = pd.read_csv("data.csv")
df.head(5)
~ Talvez seja interessante dar um CRTL+ para dar zoom em algumas imagems ~~*
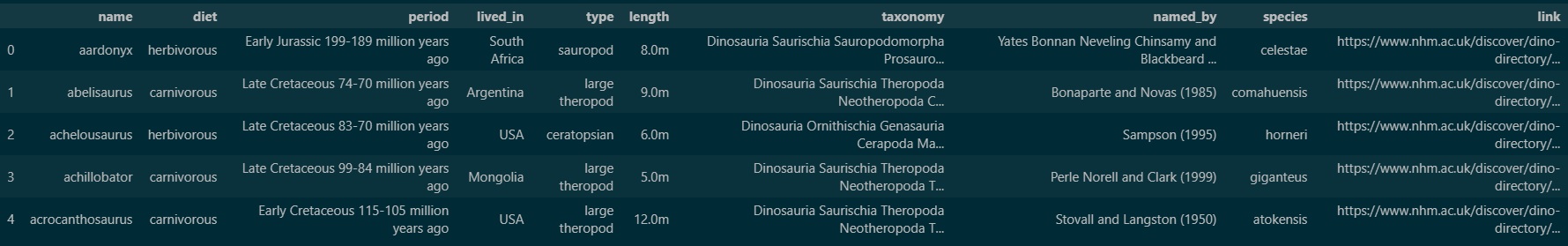
Verificamos algumas informações sobre a tabela.
df.columns
Index(['name', 'diet', 'period', 'lived_in', 'type', 'length', 'taxonomy',
'named_by', 'species', 'link'],
dtype='object')
df.info()
<class 'pandas.core.frame.DataFrame'>
RangeIndex: 309 entries, 0 to 308
Data columns (total 10 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 name 309 non-null object
1 diet 309 non-null object
2 period 309 non-null object
3 lived_in 308 non-null object
4 type 309 non-null object
5 length 291 non-null object
6 taxonomy 309 non-null object
7 named_by 309 non-null object
8 species 304 non-null object
9 link 309 non-null object
dtypes: object(10)
memory usage: 24.3+ KB
Podemos verificar o tamanho e algumas informações de nosso dataset.
Constitui-se majoritariamente de dados qualitativos, porém temos uma coluna chamada comprimento (length),
o que pode indicar ser uma variável quantitativa (numérica).
nRow, nCol = df.shape
print(f'Temos {nRow} linhas e {nCol} colunas')
print('\n')
print(df.info())
Temos 309 linhas e 10 colunas
<class 'pandas.core.frame.DataFrame'>
RangeIndex: 309 entries, 0 to 308
Data columns (total 10 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 name 309 non-null object
1 diet 309 non-null object
2 period 309 non-null object
3 lived_in 308 non-null object
4 type 309 non-null object
5 length 291 non-null object
6 taxonomy 309 non-null object
7 named_by 309 non-null object
8 species 304 non-null object
9 link 309 non-null object
dtypes: object(10)
memory usage: 24.3+ KB
None
df.isna().sum() #alguns dados faltantes, é sempre bom procurar uma maneira de tratá-los logo que possível, embora eu não tenha feito isso nesse momento.
name 0
diet 0
period 0
lived_in 1
type 0
length 18
taxonomy 0
named_by 0
species 5
link 0
dtype: int64
É possível isolar uma variável de interesse e aplicar alguma função em cima dela, como no caso value_counts, para visualizarmos como os dados dessa coluna se agrupam.
s = df['diet']
counts = s.value_counts()
percent = s.value_counts(normalize=True)
percent100 = s.value_counts(normalize=True).mul(100).round(1).astype(str) + '%'
s = pd.DataFrame({'counts': counts, 'per': percent, 'per100': percent100})[:5]
print(s)
counts per per100
herbivorous 185 0.598706 59.9%
carnivorous 94 0.304207 30.4%
omnivorous 27 0.087379 8.7%
unknown 2 0.006472 0.6%
herbivorous/omnivorous 1 0.003236 0.3%
A partir de agora podemos partir para análise gráfica. Vamos começar com a variável “diet”.
Na tabela acima percebemos que alguns dados podem não acrescentar valor à análise, como “unkown” e “herbivorous/omnivorous”. Como é apenas uma análise exploratória, não há tanto problema em excluir dados desta maneira.
df.drop(df[df['diet'] == "unknown"].index, inplace = True) #dropando variáveis sem significância
df.drop(df[df['diet'] == "herbivorous/omnivorous"].index, inplace = True)
df['diet'].value_counts() #contando os conjuntos dentro dessa variável
sns.set_style("ticks")
plt.figure(figsize = (8, 6))
sns.countplot(data=df, x='diet',palette="viridis_r", order=df['diet'].value_counts().index) #construindo um plot de contagem, no eixo x a variável de interesse e no y o porteado da função de contagem
sns.despine(offset=10, trim=True);
plt.xlabel("Dieta",fontsize=11, labelpad=10)
plt.ylabel("Contagem",fontsize=11, labelpad=10)
plt.xticks(fontsize = 11)
plt.yticks(fontsize = 11)
plt.plot()
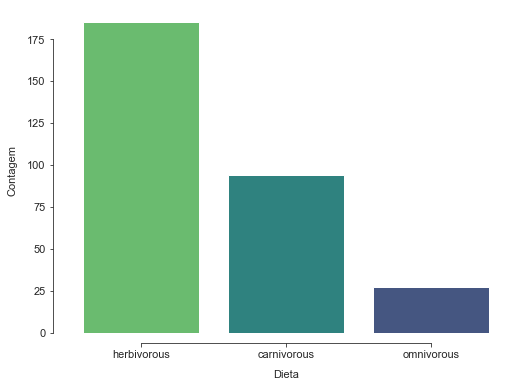
Podemos perceber que “length” é uma variável quantitativa, porém o fato dela conter uma string(m) acompanhando pode ser um empecilho, dependendo do que se deseja trabalhar em cima desta variável.
df['length'].value_counts()
6.0m 21
2.0m 19
5.0m 19
9.0m 19
3.0m 16
..
1.1m 1
0.9m 1
25.0m 1
6.8m 1
4.1m 1
Name: length, Length: 72, dtype: int64
plt.figure(figsize = (12, 6))
print('Comprimento')
print(df['length'].value_counts().sort_values(ascending=False) \
/ df['length'].value_counts().sort_values(ascending=False).sum())
sns.countplot(data=df, y='length', order=df['length'].value_counts().head(25).index, palette="viridis_r")
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
plt.xlabel("Contagem", fontsize=11, labelpad=10)
plt.ylabel("Porte: comprimento (metros)", fontsize=11, labelpad=10)
plt.xticks(fontsize = 11)
plt.yticks(fontsize = 11)
plt.title('Ranking de Tamanho: Quantidade')
plt.plot()
Comprimento
6.0m 0.072664
2.0m 0.065744
5.0m 0.065744
9.0m 0.065744
3.0m 0.055363
...
28.0m 0.003460
4.6m 0.003460
26.0m 0.003460
22.0m 0.003460
4.1m 0.003460
Name: length, Length: 72, dtype: float64
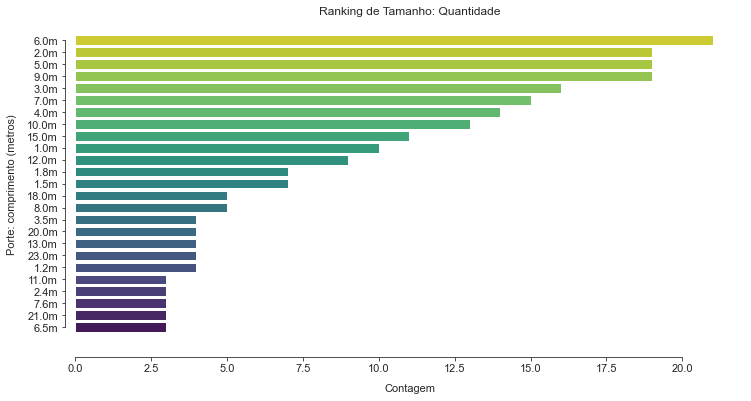
Como visto, houve mistura de strings (letras) com int (números).
Irei dropar a string “m” de type e depois transformar essa variável para numérica
(talvez isto não fosse necessário para essas análises, mas foi interessante para aprender a usar o método de separação).
df['length'] = df['length'].str.replace('m','')
df['length'] = pd.to_numeric(df['length'])
df.head(2)
df.info()
<class 'pandas.core.frame.DataFrame'>
Int64Index: 306 entries, 0 to 308
Data columns (total 10 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 name 306 non-null object
1 diet 306 non-null object
2 period 306 non-null object
3 lived_in 305 non-null object
4 type 306 non-null object
5 length 289 non-null float64
6 taxonomy 306 non-null object
7 named_by 306 non-null object
8 species 301 non-null object
9 link 306 non-null object
dtypes: float64(1), object(9)
memory usage: 34.4+ KB
Dropei as colunas taxonomy e link, pois não irei explorá-las. Verifiquei os valores max e min da variável length, assim podemos localizar a linha a qual estão contidas esses valores e verificá-los individualmente.
df.drop(['taxonomy',"link"], axis='columns', inplace=True)
print(df['length'][df.length== df.length.max()])
print(df['length'][df.length== df.length.min()])
print("\n")
print(df.loc[74].to_markdown())
30 35.0
273 35.0
Name: length, dtype: float64
74 0.25
Name: length, dtype: float64
| | 74 |
|:---------|:-------------------------------------------|
| name | confuciusornis |
| diet | carnivorous |
| period | Early Cretaceous 127-121 million years ago |
| lived_in | China |
| type | small theropod |
| length | 0.25 |
| named_by | Hou Zhou Gu and Zhang (1995) |
| species | sanctus |
Já com essa verificação, podemos ver que a subordem Sauropoda é a que apresenta os maiores indivíduos.
print(df.loc[30].to_markdown())
print("\n")
print(df.loc[273].to_markdown())
| | 30 |
|:---------|:-------------------------------------|
| name | argentinosaurus |
| diet | herbivorous |
| period | Late Cretaceous 90 million years ago |
| lived_in | Argentina |
| type | sauropod |
| length | 35.0 |
| named_by | Bonaparte and Coria (1993) |
| species | huinculensis |
| | 273 |
|:---------|:-------------------------------------------|
| name | supersaurus |
| diet | herbivorous |
| period | Early Cretaceous 154-142 million years ago |
| lived_in | USA |
| type | sauropod |
| length | 35.0 |
| named_by | Jansen (1985) |
| species | vivianae |
print(np.sort(df['length'].unique())) #verificando a extensão da diversidade de valores
[ 0.25 0.45 0.5 0.6 0.65 0.8 0.9 1. 1.1 1.2 1.3 1.4
1.5 1.6 1.7 1.8 2. 2.1 2.3 2.37 2.4 2.5 3. 3.4
3.5 4. 4.1 4.2 4.4 4.5 4.6 4.7 5. 5.3 5.5 5.7
6. 6.2 6.4 6.5 6.6 6.8 7. 7.4 7.5 7.6 8. 8.1
8.2 8.5 8.6 9. 10. 11. 12. 12.5 13. 14. 15. 17.
18. 20. 21. 21.5 22. 23. 24. 25. 26. 28. 30. 35.
nan]
Podemos fazer um agrupamento dos dados quantitativos de comprimento em grupos qualitativos.
Resolvi agrupá-los em 5 grupos e depositá-los em uma nova coluna, para facilitar a visualização.
A presença de muitos grupos normalmente torna difícil a interpretação e perde seu valor didático.
porte = []
for value in df["length"]:
if value < 1.0:
porte.append("Muito Pequeno")
elif 2.5 >= value and value >= 1.0:
porte.append("Pequeno")
elif 7.0 >= value and value >= 2.6:
porte.append("Medio")
elif 14.0 >= value and value >= 7.1:
porte.append("Grande")
elif value > 14.1:
porte.append("Gigante")
else:
porte.append("NAN") #o restante ficará aqui, provavelmente serão erros de preenchimento da coluna
df["porte"] = porte
print(df["porte"])
0 Grande
1 Grande
2 Medio
3 Medio
4 Grande
...
304 Gigante
305 Medio
306 Medio
307 Pequeno
308 NAN
Name: porte, Length: 306, dtype: object
Se temos dados, temos perguntas, e podemos respondê-las procurando relações entre estes dados.
- Será que existe correlação entre tamanho e dieta? E entre tamanho e as diferentes Subordens?
- Criarei um gráfico de dispersão para analisar a distribuição dos grupos que acabamos de criar em relação à dieta.
plt.figure(figsize=(15,9))
sns.set_style("ticks")
sns.swarmplot(x='diet',
y='length',
data=df,
hue='porte',
split=True,
palette="Set1",
alpha=.8, s=10,linewidth=1.0)
sns.despine(offset=10, trim=True) #estilizando os eixos
# Ajustando o tamanho do y
plt.ylim(-1, 40)
# Ajustando o tamanho dos dados de cada eixo
plt.xlabel("Dieta", fontsize=11, labelpad=10)
plt.ylabel("Porte: comprimento (metros)", fontsize=11, labelpad=10)
plt.xticks(fontsize = 11)
plt.yticks(fontsize = 11)
# Ajustando a legenda
plt.legend(bbox_to_anchor=(1, 1), loc=2, borderpad=1, labelspacing=1.2,fontsize=12)
<matplotlib.legend.Legend at 0x1cd69635040>
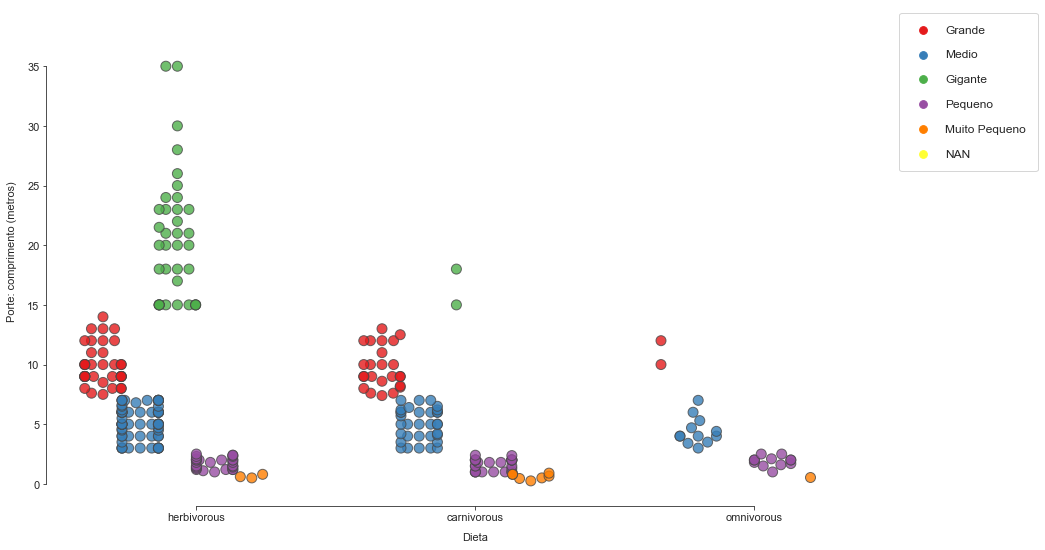
No gráfico acima podemos perceber que há grande diversidade nos grupos de herbívoros, e nestes apresentando a grande maioria de espécies gigantes.Este gráfico nos permite observar a distribuição de uma variável em outra e também a densidade de determinado valor. Os pontos mais escuros normalmente expressam maior densidade nessa área; em um dataset maior a densidade tende a tornar-se mais visível.
Podemos tentar analisar qual o padrão de tamanho em relação às Subordens.
plt.figure(figsize=(15,9))
df.drop(df[df['type'] == "1.0m"].index, inplace = True) # dropando um erro de preenchimento da planilha "type"
sns.set_style("ticks")
sns.swarmplot(x='type',
y='length',
data=df,
hue='porte',
split=True, #separando pelo hue
palette="Set1",
alpha=.8, s=10,linewidth=1.0)
sns.despine(offset=10, trim=True) #estilizando os eixos
# Ajustando o tamanho do y
plt.ylim(-1, 40)
# Ajustando o tamanho dos dados de cada eixo
plt.xlabel("Tipo: Subordem", fontsize=11, labelpad=10)
plt.ylabel("Porte: comprimento (metros)", fontsize=11, labelpad=10)
plt.xticks(fontsize = 11)
plt.yticks(fontsize = 11)
# Ajustando a legenda
plt.legend(bbox_to_anchor=(1, 1), loc=2, borderpad=1, labelspacing=1.2,fontsize=12)
<matplotlib.legend.Legend at 0x1cd68bfc550>
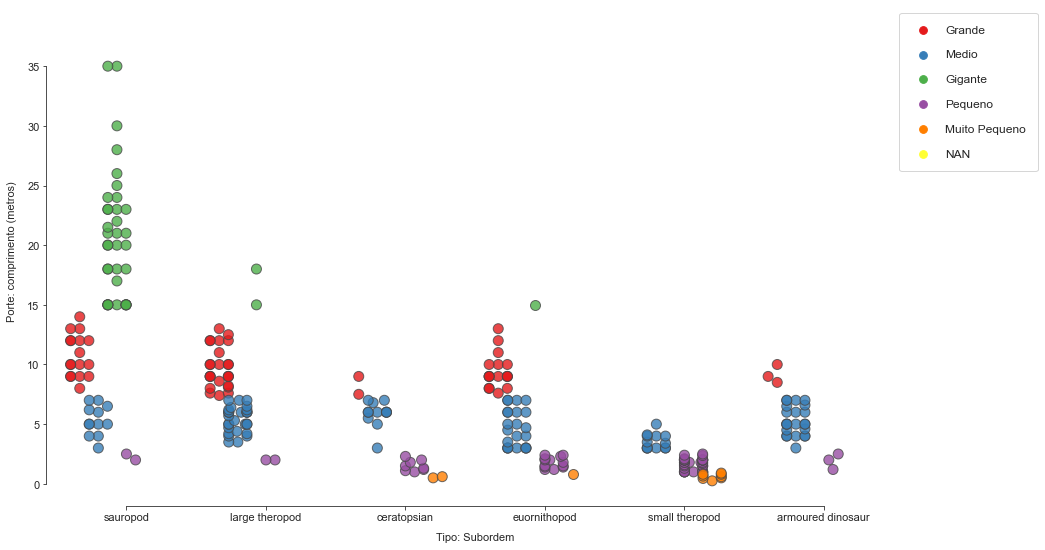
Um histograma apontando a relação das subordem com a dieta também pode ser interessante visualizar.
plt.figure(figsize=(15,9))
sns.histplot(binwidth=0.5, x="type", hue="diet", data=df, stat="count", multiple="stack",palette="cubehelix")
plt.xticks(fontsize = 15)
plt.yticks(fontsize = 15)
plt.xlabel("Tipo: Subordem", fontsize=11, labelpad=10)
plt.ylabel("Contagem", fontsize=11, labelpad=10)
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
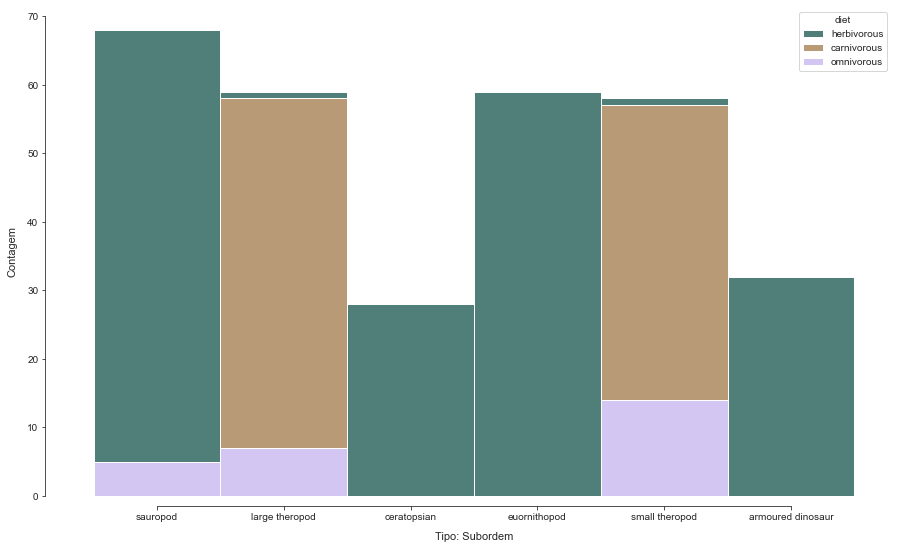
# simples análise das variáveis. Podemos ver como a análise torna-se diferente quando temos uma variável quantitativa.
print(df['type'].describe())
print("\n")
print(df['diet'].describe())
print("\n")
print(df['length'].describe())
count 306
unique 7
top sauropod
freq 68
Name: type, dtype: object
count 306
unique 3
top herbivorous
freq 185
Name: diet, dtype: object
count 289.000000
mean 7.229135
std 6.321244
min 0.250000
25% 2.400000
50% 6.000000
75% 9.000000
max 35.000000
Name: length, dtype: float64
Em relação à subordem, quais estão mais presentes no estudo?
plt.figure(figsize = (12, 6))
df['type'].value_counts()
print('Tipos: Subordem')
print(df['type'].value_counts().sort_values(ascending=False) \
/ df['type'].value_counts().sort_values(ascending=False).sum())
sns.countplot(data=df, y='type', order=df['type'].value_counts().index, palette="viridis_r")
sns.despine(offset=10, trim=True)
sns.set_style("white")
plt.title('Tipos: Subordem')
plt.plot()
# outro erro no preenchimento da coluna
Tipos: Subordem
sauropod 0.222222
small theropod 0.192810
euornithopod 0.192810
large theropod 0.192810
armoured dinosaur 0.104575
ceratopsian 0.091503
1.0m 0.003268
Name: type, dtype: float64
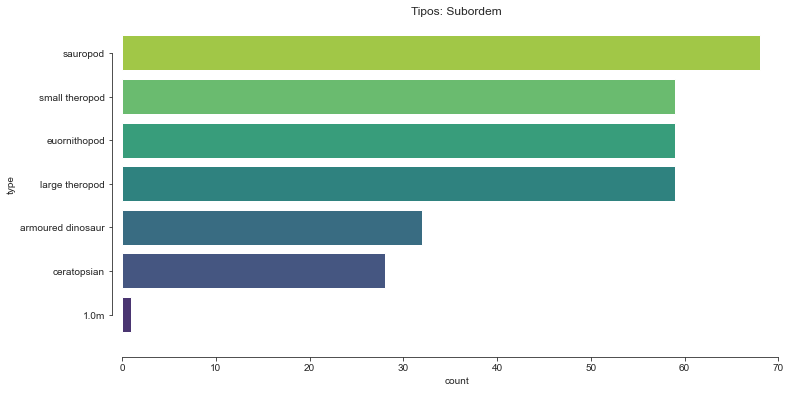
#variável com muitas classes, porém a maioria com um exemplar, normal para um banco de espécies.
count = df['species'].value_counts()
display(count)
mongoliensis 7
giganteus 3
gobiensis 3
armatus 3
gracilis 2
..
amicagraphica 1
prenes 1
australis 1
skarzynskii 1
transsylvanicus 1
Name: species, Length: 268, dtype: int64
# Podemos procurar por alguma espécie de interesse para sabermos algumas informações
df[df['species'].str.contains("rex")==True]
# Parece que rex (rei) não é um subnome aplicado a somente uma espécie. 🦎 🦖
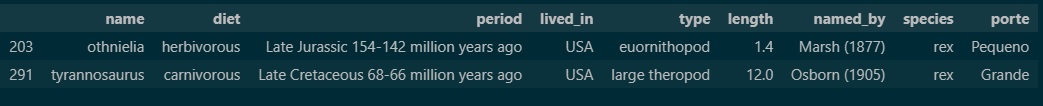
df[df['name'].str.contains("tyrannosaurus")==True]

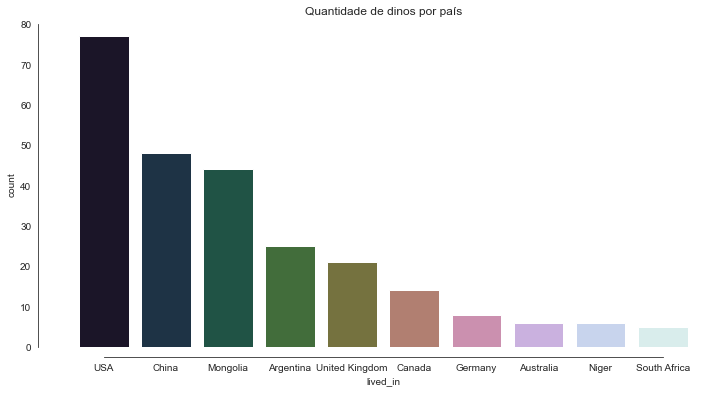
Analisando a procedência:
- Será que existiram mais dinossauros em uma região, ou será que aquela região faz mais pesquisas sobre esse nicho?
plt.figure(figsize = (12, 6))
df['lived_in'].value_counts()
print('Proporção de dinossauros por país')
print(df['lived_in'].value_counts().sort_values(ascending=False) \
/ df['lived_in'].value_counts().sort_values(ascending=False).sum())
sns.countplot(data=df, x='lived_in',palette="cubehelix", order=df['lived_in'].value_counts().head(10).index)
sns.despine(offset=10, trim=True)
sns.set_style("whitegrid")
plt.title('Quantidade de dinos por país')
plt.plot()
Proporção de dinossauros por país
USA 0.253289
China 0.157895
Mongolia 0.144737
Argentina 0.082237
United Kingdom 0.069079
Canada 0.046053
Germany 0.026316
Australia 0.019737
Niger 0.019737
South Africa 0.016447
Tanzania 0.016447
Spain 0.016447
Brazil 0.013158
France 0.013158
India 0.013158
Morocco 0.009868
Zimbabwe 0.009868
Madagascar 0.009868
Japan 0.006579
Egypt 0.006579
Russia 0.006579
Uzbekistan 0.006579
Kazakhstan 0.006579
Romania 0.006579
Malawi 0.003289
Wales 0.003289
Antarctica 0.003289
North Africa 0.003289
Tunisia 0.003289
Switzerland 0.003289
Uruguay 0.003289
Name: lived_in, dtype: float64
Análise dos períodos da “Era dos Dinossauros”.
plt.figure(figsize = (12, 6))
df['period'].value_counts()
print('Proporção de dinossauros por período')
print(df['period'].value_counts().sort_values(ascending=False) \
/ df['period'].value_counts().sort_values(ascending=False).sum())
sns.countplot(data=df, y='period', order=df['period'].value_counts().head(20).index)
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
plt.title('Quantidade de dinos por período')
plt.plot()
Proporção de dinossauros por período
Late Cretaceous 76-74 million years ago 0.045902
Late Cretaceous 84-71 million years ago 0.029508
Early Cretaceous 121-99 million years ago 0.029508
Early Cretaceous 127-121 million years ago 0.029508
Late Jurassic 154-142 million years ago 0.026230
...
Early Cretaceous 121-97 million years ago 0.003279
Early Cretaceous 126-142 million years ago 0.003279
Early Jurassic 170 million years ago 0.003279
Late Triassic 205-195 million years ago 0.003279
USA 0.003279
Name: period, Length: 151, dtype: float64
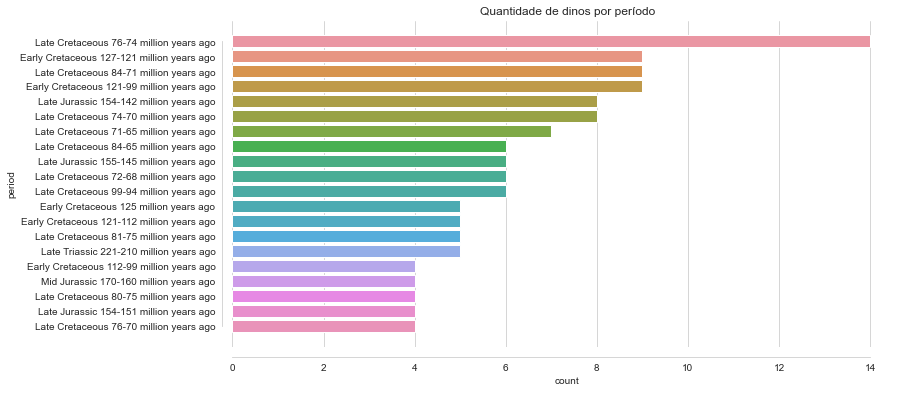
Temos muitos períodos similares que divergem em relação a “alguns” milhões de anos (e.g. Early Cretaceous 121-99 million years ago - Early Cretaceous 127-121 million years ago). Talvez possamos agrupar alguns espaços de tempo para facilitar a análise.
df.head(2) #A informação de anos junto dos períodos acaba criando muitos grupos diferentes

Clusterizando os períodos em Early, Mid e Late, sem a exatidão dos anos. Chamei o método str.split para pegar o que havia antes do 2º espaço e colocar em uma nova coluna.
df["periodo_grupos"] = df["period"].str.split(" ").str[:2].str.join(" ")
df.head(2)

# Printando contagem (%) e plotando
plt.figure(figsize = (12, 6))
df['periodo_grupos'].value_counts()
print('Proporção de dinossauros por Período')
print(df['periodo_grupos'].value_counts().sort_values(ascending=False) \
/ df['periodo_grupos'].value_counts().sort_values(ascending=False).sum())
sns.countplot(data=df, y='periodo_grupos', order=df['periodo_grupos'].value_counts().index, palette="magma")
sns.despine(offset=10, trim=True);
sns.set_style("ticks")
plt.title('Proporção de dinossauros por Período')
plt.plot()
# parece que alguém preencheu a coluna period com um dado geográfico.
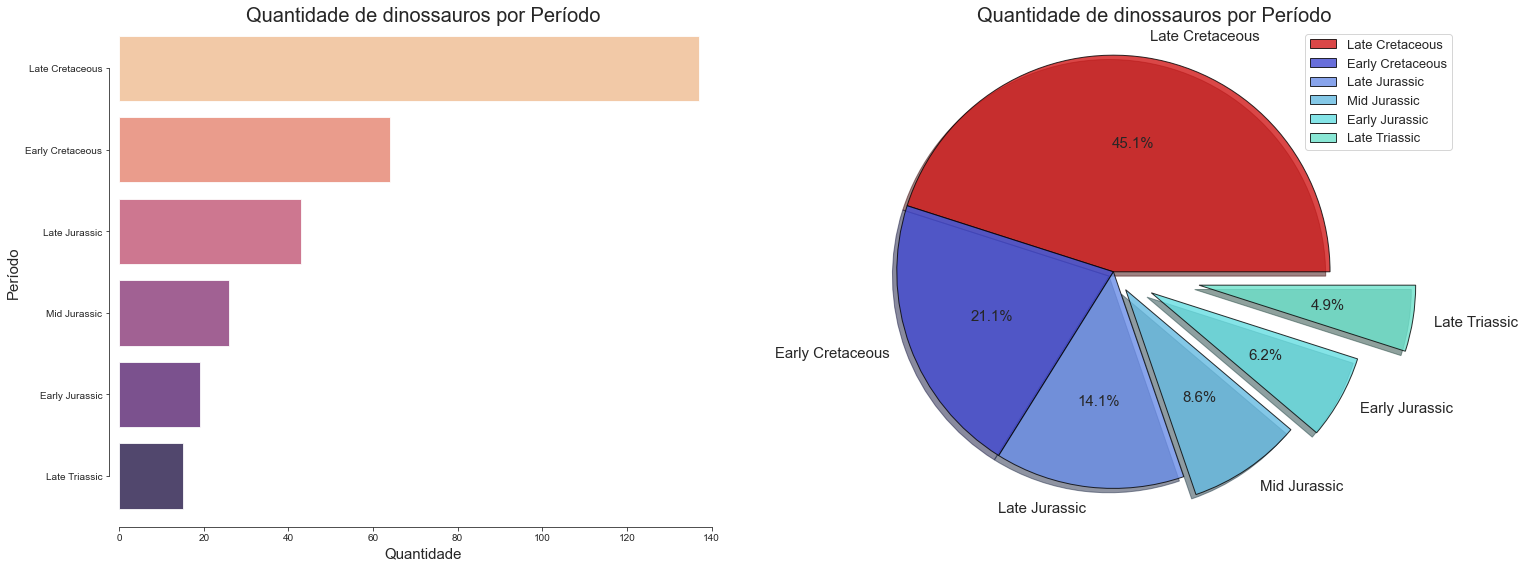
Proporção de dinossauros por Período
Late Cretaceous 0.449180
Early Cretaceous 0.209836
Late Jurassic 0.140984
Mid Jurassic 0.085246
Early Jurassic 0.062295
Late Triassic 0.049180
USA 0.003279
Name: periodo_grupos, dtype: float64
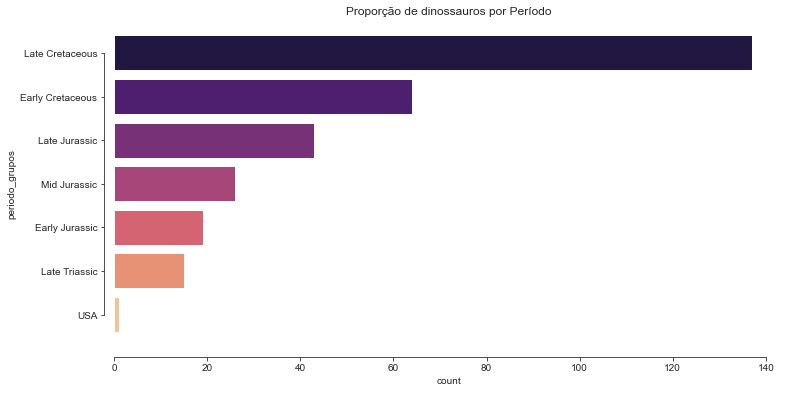
Irei dropar a linha com USA. Poderia ter utilizado uma alternativa melhor para tratamento, e assim não perder aquele dado por causa de um erro, mas foi a medida mais rápida para a plotagem.
df.drop(df[df['periodo_grupos'] == "USA"].index, inplace = True)
Criando um gráfico mais elaborado na visualização dos períodos
- Podemos ver que o Cretáceo foi a era de ouro dos dinossauros, diferente do que se acredita, baseado nos filmes.
- É possível pensar que essa maior quantidade também seja em razão de melhores condições de preservação dos fósseis e outros determinantes.
count = df["periodo_grupos"].value_counts().values
anos = df["periodo_grupos"].value_counts().index
plt.figure(figsize = (24, 9))
plt.subplot(1, 2, 1)
sns.countplot(data=df, y='periodo_grupos', order=df['periodo_grupos'].value_counts().index, palette="magma_r", alpha = 0.8,)
sns.despine(offset=10, trim=True);
sns.set_style("ticks")
plt.xlabel("Quantidade", fontsize=15)
plt.ylabel("Período", fontsize=15)
plt.title("Quantidade de dinossauros por Período",fontsize=20)
plt.subplot(1, 2, 2)
plt.pie(count,
autopct='%1.1f%%',
shadow=True, startangle=0,
labels = anos,
colors = ["#d11919", "#424ad1", "#6a8ee8", "#66bbe2", "#66dee2", "#6ce2cb", "#6ad187", "#3b7f5b"],
labeldistance = 1.1,
explode = [0, 0,0, .1, .2, .4],
wedgeprops = {"ec": "k", 'alpha':0.8},
textprops = {"fontsize": 15},
)
plt.axis("equal")
plt.title("Quantidade de dinossauros por Período",fontsize=20)
plt.legend(prop={'size': 13})
<matplotlib.legend.Legend at 0x1cd64bad910>
Por último, também podemos explorar os pesquisadores (named_by) mais ativos na área.
- Farei a mesma limpeza de string separando o nome da data.
df['autor'] = [x.split('(')[0] for x in df['named_by']] #Salvei apenas o que tinha antes do () em uma nova variável
# porém isso salvou os nomes com um espaço depois da última letra
df['ano'] = df['named_by'].str.extract('(\d+)', expand=False)
df.loc[df['ano'].notnull(), 'ano'] = df.loc[df['ano'].notnull(), 'ano'].apply(int)
df.info()
#outras medidas:
#df['ano'] =df['named_by'].str.replace(r'[^(]*\(|\)[^)]*', '') # Peguei apenas o que tinha dentro do () e coloquei como ano de descoberta, não funcionou bem
#df['ano'] =df['named_by'].apply(lambda st: st[st.find("(")+1:st.find(")")])
#pd.to_datetime(df.ano, format='%Y')
<class 'pandas.core.frame.DataFrame'>
Int64Index: 304 entries, 0 to 308
Data columns (total 12 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 name 304 non-null object
1 diet 304 non-null object
2 period 304 non-null object
3 lived_in 304 non-null object
4 type 304 non-null object
5 length 288 non-null float64
6 named_by 304 non-null object
7 species 299 non-null object
8 porte 304 non-null object
9 periodo_grupos 304 non-null object
10 autor 304 non-null object
11 ano 299 non-null object
dtypes: float64(1), object(11)
memory usage: 39.0+ KB
df.head(2)

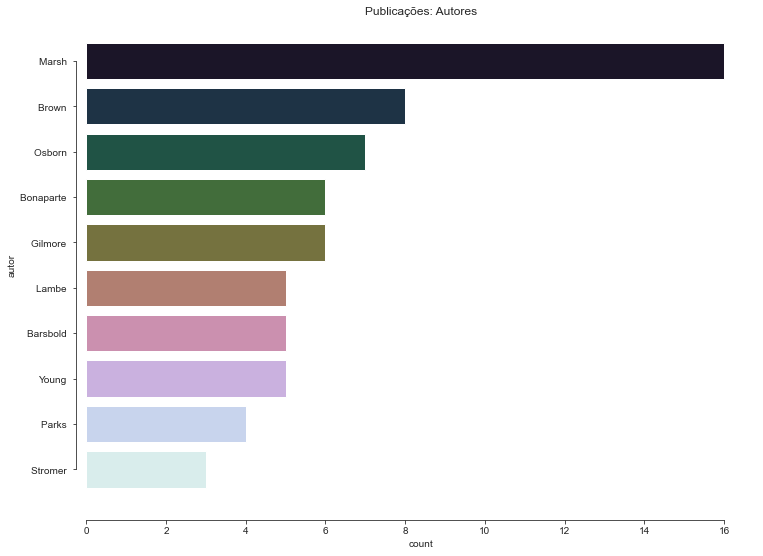
Quais autores fizeram mais descobertas?
count = df['autor'].value_counts().head(10)
display(count)
plt.figure(figsize=(12,9))
sns.countplot(data=df, y='autor', order=df['autor'].value_counts().head(10).index, palette="cubehelix")
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
plt.title('Publicações: Autores')
plt.plot()
Marsh 16
Brown 8
Osborn 7
Bonaparte 6
Gilmore 6
Lambe 5
Barsbold 5
Young 5
Parks 4
Stromer 3
Name: autor, dtype: int64
count.dtype
dtype('int64')
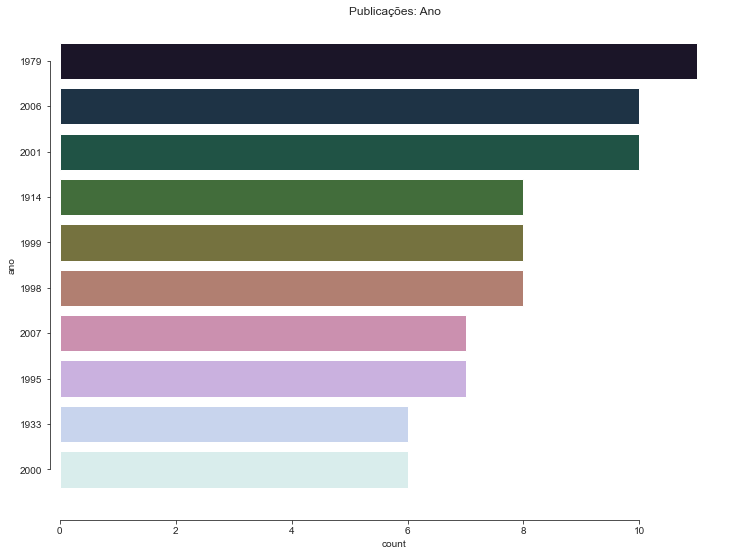
Podemos verificar os anos de maiores descobertas.
plt.figure(figsize=(12,9))
sns.countplot(data=df, y='ano', order=df['ano'].value_counts().head(10).index, palette="cubehelix")
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
plt.title('Publicações: Ano')
plt.plot()
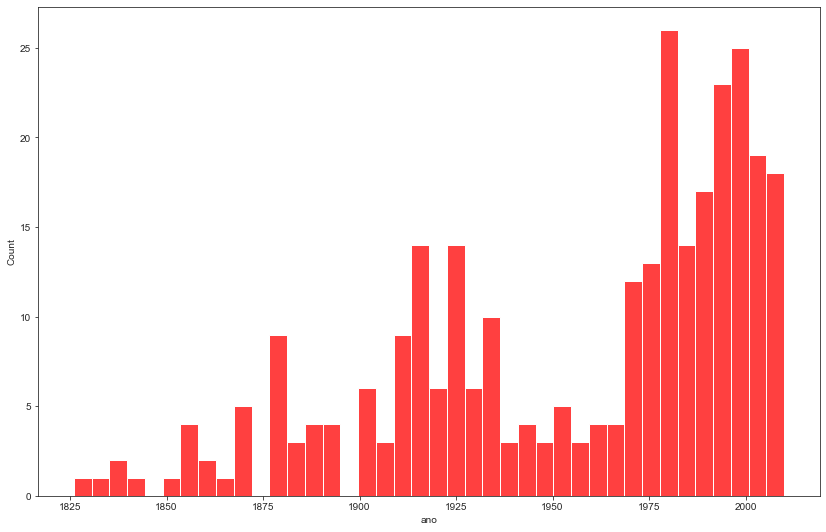
Criando uma análise temporal baseada em um conjunto de tempos representados por cada barra.
Interessante verificar que, caso eu aumente/diminua o nº de bins, o gráfico modifica e, assim, sua interpretação também. Quando modifico, a barra leva uma média de um conjunto de datas próximas. Assim, se o top1 apresentar alto valor, mas a data vizinha que participa desse conjunto da barra for um valor baixo, esse conjunto pode ser menor que conjuntos de datas que não apresentaram tantos outliers. Veja a diferença no próximo plot. Pelo que entendi, essas barras são baseadas em média, medida essa que é influenciada por outliers.
plt.figure(figsize=(14,9))
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
sns.histplot(data=df, x="ano", bins=40, color='red')
plt.plot()
plt.figure(figsize=(14,9))
sns.despine(offset=10, trim=True)
sns.set_style("ticks")
sns.histplot(data=df, x="ano", bins=50, color='red')
plt.plot()
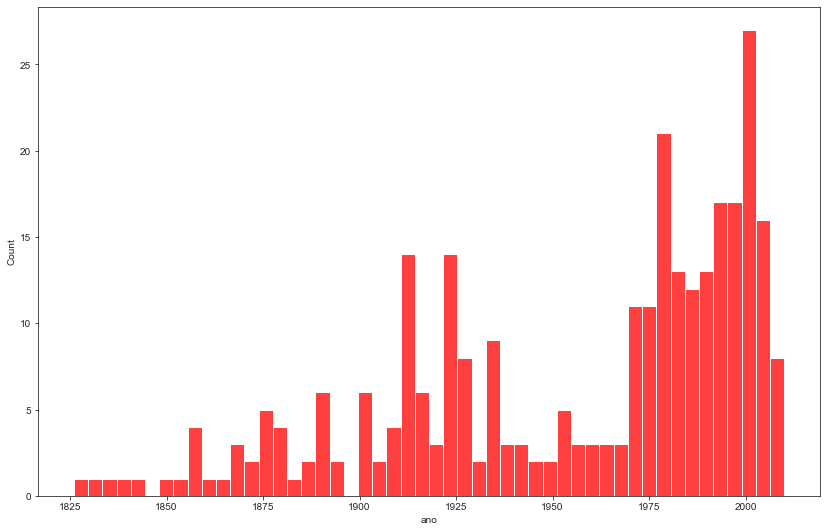
Podemos criar um dicionário unindo duas colunas, ele apresentará uma “chave” e seu “valor”, representados pelas duas variáveis de escolha. Isto é interessante para isolar áreas de interesse e, dependendo da análise, pode facilitar a implementação da metodologia aplicada.
area_dict = dict(zip(df.autor, df.ano))
area_dict
{'Yates Bonnan Neveling Chinsamy and Blackbeard 2010 ': 2010,
'Bonaparte and Novas ': 1985,
'Sampson ': 1995,
'Perle Norell and Clark ': 1999,
'Stovall and Langston ': 1950,
'Stromer ': 1915,
'Sereno Wilson Larsson Dutheil and Sues ': 1944,
'Peng ': 1990,
'Gilmore ': 1913,
'Ryan 2007': 2007,
'Lamb ': 1914,
'Kurzanov ': 1992,
'Marsh ': 1889,
'Bonaparte ': 1979,
'Salgado and Bonaparte ': 1991,
'Le Loeuff ': 1995,
'Cabrera ': 1947,
'Brown ': 1912,
'Barsbold ': 1986,
'von Huene ': 1927,
'Sanz Buscalioni Casanovas and Sanafé ': 1987,
'Rozhdestvensky ': 1966,
'Dong and Azuma ': 1990,
'Mayer ': 1861,
'Russell ': 1970,
'Bonaparte and Coria ': 1993,
'Parks ': 1922,
'Rich and Rich ': 1989,
'Coria Chiappe and Dingus ': 2002,
'Longman ': 1926,
'Dodson ': 1986,
'Maryanska and Osmolska ': 1975,
'Burnham Derstler Currie Bakker Zhou and Ostrom ': 2000,
'Jain Kutty Roy-Chowdhury and Chatterjee ': 1975,
'Charig and Milner ': 1987,
'Paul ': 1988,
'Xu Tang and Wang ': 1999,
'Osmólska ': 1987,
'Riggs ': 1903,
'C. M. Sternberg ': 1953,
'Rauhut Remes Fechner Cladera and Puerta ': 2005,
'Makovicky Apesteguía & Agnolin ': 2005,
'Cope ': 1866,
'Ji Currie Norell and Ji. ': 1998,
'Carpenter Kirkland Burge and Bird ': 2001,
'apertus': nan,
'Phillips ': 1871,
'Zhao Cheng and Xu ': 1999,
'belli': nan,
'Long and Murry ': 1995,
'Yeh ': 1975,
'Corro ': 1974,
'Dong Zhou and Zhang ': 1983,
'Clark Norell and Barsbold ': 2001,
'bauri': nan,
'Wagner ': 1859,
'Hou Zhou Gu and Zhang ': 1995,
'Hammer and Hickerson ': 1994,
'Lucas ': 1902,
'Dong and Tang ': 1985,
'Osmólska and Roniewicz ': 1970,
'Ostrom ': 1970,
'Sereno Duthiel Iarochene Larsson Lyon Magwene Sidor Varricchio and Wilson ': 1996,
'Janensch ': 1914,
'wetherilli': nan,
'Matthew and Brown ': 1922,
'Allain ': 2005,
'Sternberg ': 1937,
'Lambe ': 1913,
'Haubold ': 1991,
'Kirkland ': 1998,
'Sereno Forster Rogers and Monetta ': 1993,
'Hutt Naish Martill Barker and Newberry ': 2001,
'You Luo Shubin Witmer Tang and Tang ': 2003,
'Ksepka and Norell ': 2006,
'Perle vide Barsbold and Perle ': 1980,
'Wiman ': 1929,
'tutus': nan,
'Sander Mateus Laven and Knötschke ': 2006,
'Walker ': 1964,
'Azuma and Currie ': 2000,
'Kobayashi and Azuma ': 2003,
'Osmólska Roniewicz and Barsbold ': 1972,
'Carpenter Miles and Cloward ': 2001,
'Coria and Salgado ': 1995,
'Brett-Surman ': 1979,
'Vickaryous Russell Currie and Zhao ': 2001,
'Perle Maryańska and Osmólska ': 1982,
'Sereno ': 2000,
'Bonaparte Ferigolo and Ribeiro ': 1999,
'Xu Clark Forster Norell Erickson Eberth Jia and Zhao ': 2006,
'Leidy ': 1856,
'Hatcher ': 1903,
'Barsbold and Perle ': 1984,
'Reig ': 1963,
'Crompton and Charig ': 1962,
'Maryańska and Osmólska ': 1974,
'Dong Tang and Zhou ': 1982,
'Mantell ': 1850,
'Huxley ': 1869,
'Boulenger and van Beneden ': 1881,
'Huene and Matley ': 1933,
'Martill Cruickshank Frey Small and Clarke ': 1996,
'Jain and Bandyopadhyay ': 1997,
'Wild ': 1991,
'Riabinin ': 1939,
'Zhang and Yang ': 1995,
'Wang and Xu ': 2001,
'Sereno Beck Dutheil Larsson Lyon Moussa Sadleir Sidor Varricchio Wilson and Wilson ': 1999,
'Göhlich & Chiappe ': 2006,
'Hennig ': 1915,
'Yadagiri ': 1988,
'Xu Makovicky Wang Norell and You ': 1960,
'Bonaparte González Riga and Apesteguía ': 2006,
'Huene ': 1910,
'Ezcurra and Cuny 2007 ': 2007,
'Young ': 1942,
'Taquet & Russell ': 1999,
'Haughton ': 1924,
'Nopcsa ': 1902,
'Horner and Makela ': 1979,
'Sues & Taquet ': 1979,
'Coria and Currie ': 2006,
'Madsen ': 1976,
'Sampson Carrano & Forster ': 2001,
'Owen ': 1868,
'Kellner et al. ': 2006,
'Ritgen ': 1826,
'Bohlin ': 1953,
'Dong ': 1979,
'Xu Zhou and Wang ': 2000,
'Molnar ': 1980,
'Zhao and Currie ': 1993,
'Bonaparte and Vince ': 1979,
'Bartholomai and Molnar ': 1981,
'Lull ': 1905,
'Nowinski ': 1971,
'Hutt Martill and Barker ': 1996,
'Lydekker ': 1893,
'Sereno Beck Dutheil Larsson Lyon Moussa Sadleir Sidor Varricchio Wilson & Wilson ': 1999,
'Nagao ': 1936,
'Bonaparte and Powell ': 1980,
'Barsbold Osmólska Watabe Currie and Tsogtbaatar ': 2000,
'Kirkland and Wolfe ': 2001,
'de Klerk Forster Sampson Chinsamy and Ross ': 2000,
'Borsuk-Bialynicka ': 1977,
'Osbourne ': 1933,
'Horner and Weishampel ': 1988,
'Varricchio Marin and Katsura ': 2007,
'Taquet ': 1976,
'Osborn ': 1924,
'Brown and Schlaikjer ': 1943,
'Galton Yates and Kermack 2007 ': 2007,
'Smith Lamanna Lacovara Dodson Smith Poole Giegengack and Attia ': 2001,
'Pérez-Moreno Sanz Buscalioni Moratalla Ortega and Rasskin-Gutman ': 1994,
'Meyer ': 1857,
'Talbot ': 1911,
'Eudes-Deslongchamps ': 1838,
'Hulke ': 1881,
'Woodward ': 1910,
'Fraas ': 1913,
'Ji and Ji ': 1996,
'Granger and Gregory ': 1923,
'Head ': 1998,
'Kurzanov and Bannikov ': 1983,
'Lavocat ': 1954,
'Matherton ': 1869,
'Sereno Wilson and Conrad ': 2004,
'Maryañska ': 1977,
'Andrews ': 1921,
'Chure ': 1996,
'Colbert ': 1970,
'Camp ': 1936,
'Perle ': 1979,
'Tumanova ': 1993,
'Turner Hwang and Norell ': 2007,
'Hu ': 1973,
'Chiappe Norell and Clark ': 1998,
'Eaton ': 1960,
'Ji Ji Lü and Yuan ': 2007,
'Xu Wang and Wu ': 1999,
'Xu Norell Wang Makovicky and Wu ': 2002,
'Gao ': 1992,
'Xu Zhang Tan Zhao and Tan ': 2006,
'Bunzel ': 1871,
'Sereno Beck Dutheil Gado Larsson Lyon Marcot Rauhut Sadleir Sidor Varricchio Wilson and Wilson ': 1998,
'Jansen ': 1985,
'Maleev ': 1956,
'Morris ': 1843,
'Galton and Jensen ': 1979,
'Dong Li Zhou and Zhang ': 1973,
'Novas and Puerta ': 1997,
'Averianov and Sues ': 2007,
'Kirkland Gaston and Burge ': 1993,
'Galton ': 1975,
'Raath ': 1972,
'He ': 1979,
'Dong Chang Li and Zhou ': 1978,
'Bai Yang and Wang ': 1990,
'Watanabe ': 1992,
'Xu Forster Clark and Mo ': 2006,
'Lü Li Ji Wang Zhang and Dong ': 2006,
'Sues ': 1980,
'Wolfe and Kirkland ': 1998}
print(area_dict.get("Marsh ")) #trará seu valor
1889
Outra possibilidade é transformar nossos dados em conjuntos “arrays”. Normalmente se faz isso na hora de organizar nossos dados para implementar algum modelo preditivo.
arr = df["ano"].to_numpy()
arr = arr[~pd.isnull(arr)] #removendo nans
print(arr)
[1826 1833 1837 1838 1843 1850 1854 1856 1857 1858 1859 1861 1866 1868
1869 1869 1871 1871 1877 1877 1877 1877 1877 1878 1879 1881 1881 1884
1885 1885 1889 1889 1890 1890 1891 1891 1893 1894 1900 1902 1902 1902
1903 1903 1905 1905 1908 1910 1910 1910 1911 1912 1913 1913 1913 1913
1914 1914 1914 1914 1914 1914 1914 1914 1915 1915 1915 1916 1917 1917
1919 1920 1921 1922 1922 1922 1923 1923 1923 1923 1924 1924 1924 1924
1924 1924 1925 1926 1926 1927 1928 1928 1929 1929 1929 1931 1932 1933
1933 1933 1933 1933 1933 1934 1936 1936 1937 1939 1939 1941 1942 1943
1944 1947 1950 1950 1952 1953 1953 1954 1954 1955 1956 1958 1960 1960
1962 1963 1964 1964 1966 1968 1969 1970 1970 1970 1970 1970 1971 1972
1972 1972 1973 1973 1974 1974 1974 1974 1975 1975 1975 1975 1976 1976
1976 1977 1977 1978 1978 1978 1979 1979 1979 1979 1979 1979 1979 1979
1979 1979 1979 1980 1980 1980 1980 1980 1981 1981 1981 1981 1981 1982
1982 1983 1983 1983 1983 1984 1984 1985 1985 1985 1985 1986 1986 1986
1986 1987 1987 1987 1987 1988 1988 1988 1988 1989 1989 1990 1990 1990
1991 1991 1991 1991 1992 1992 1992 1993 1993 1993 1993 1993 1994 1994
1995 1995 1995 1995 1995 1995 1995 1996 1996 1996 1996 1996 1996 1997
1997 1997 1998 1998 1998 1998 1998 1998 1998 1998 1999 1999 1999 1999
1999 1999 1999 1999 2000 2000 2000 2000 2000 2000 2001 2001 2001 2001
2001 2001 2001 2001 2001 2001 2002 2002 2002 2003 2003 2004 2005 2005
2005 2006 2006 2006 2006 2006 2006 2006 2006 2006 2006 2007 2007 2007
2007 2007 2007 2007 2010]
E assim termina essa análise. Um pequeno dataset nos possibilitou uma boa quantidade de insights, porém dizer que o conjunto foi totalmente explorado não seria verdade.
Dentre outras análises, poderiam ser explorados de forma mais profunda:
- A relação das espécies a cada período;
- Um chart de mapas, caso se utilizasse dados de long. e lat.;
- Relação de cada autor com sua espécie descrita;
- dentre outros.
Este projeto certamente ampliou minha capacidade exploratória e meu conhecimento sobre o conteúdo analisado, e espero assim também gerar valor para quem tenha lido.
Até breve ;)